R语言学习笔记
| 阿里云国内75折 回扣 微信号:monov8 |
| 阿里云国际,腾讯云国际,低至75折。AWS 93折 免费开户实名账号 代冲值 优惠多多 微信号:monov8 飞机:@monov6 |
R语言学习笔记
一.准备环境
下载R语言和Rtoolshttps://mirrors.tuna.tsinghua.edu.cn/CRAN/
下载Rstudiohttps://posit.co/downloads/
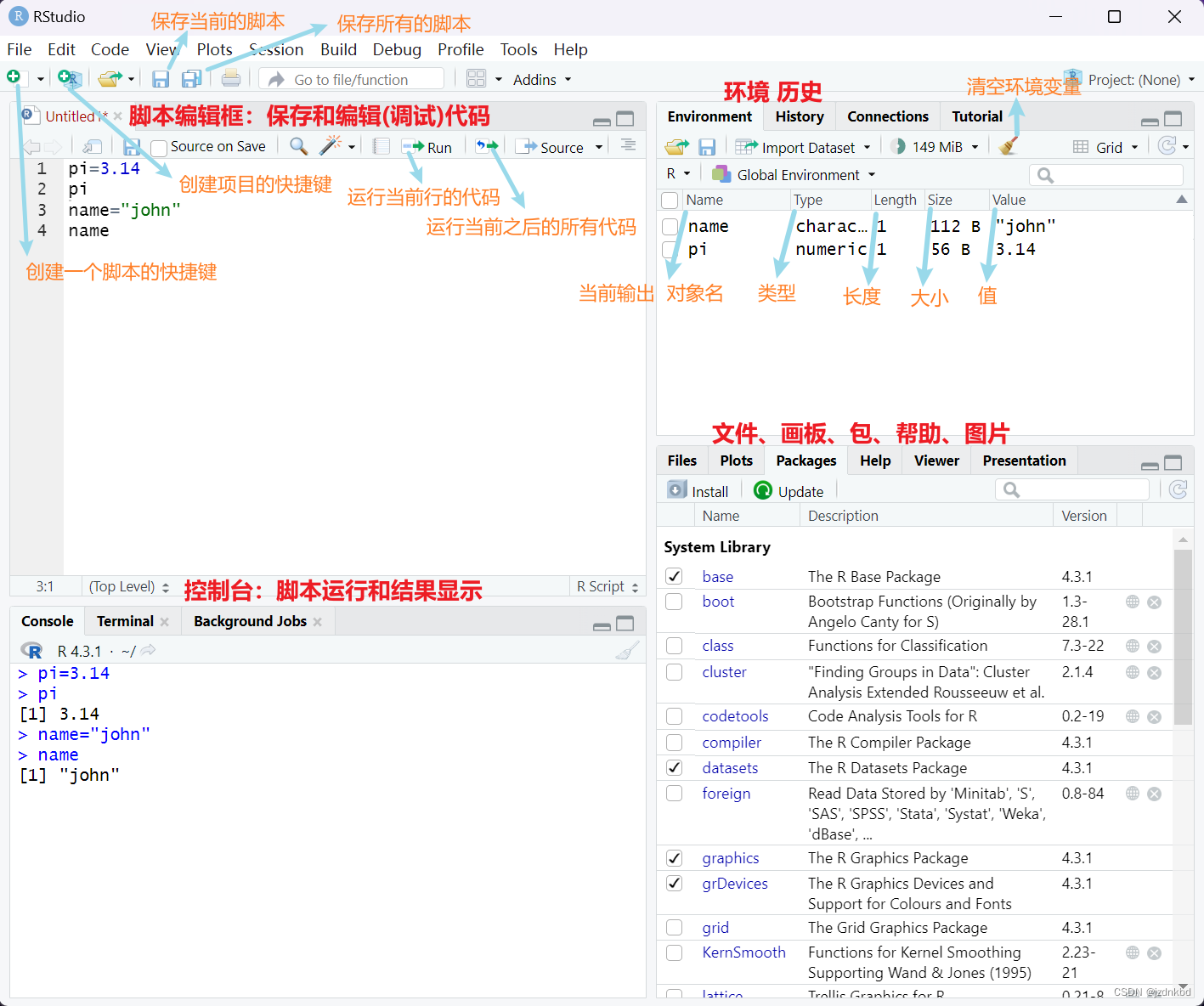
二.认识控制台
三.R包
R包并不是凭空产生的都是作者编译好函数后封装成包然后将其上传到某个平台储存。目前R包主要都可以从这三大平台下载分别是CRAN官网平台Bioconductor生信平台及Github第三方平台。
简单介绍一下三个平台。
1.CRAN存储了R最新版本的代码和文档的服务器 。这是R语言官方平台市面上常用的R包以及已经功能完整度比较高的R包基本都会上传到CRAN官方平台因此通常可以从rstudio直接用代码下载。另外可以从官网平台下载所需压缩包然后在本地进行安装。
2.生物信息学领域的Bioconductor平台它提供的R包主要为基因组数据分析和注释工具。这个平台主要上传了很多关于生信技术相关的R包如果在遇到相关R包不能从官方CRAN平台下载时可以优先考虑从这个平台下载。
3.面向开源及私有软件的第三方平台–Github。R包的作者更愿意将其存储在该平台因此很多时候需要在上面下载 。如果前两个平台都无法下载这时可以考虑第三方平台github这里包含了99%的R包。
#报错用英文显示方便出错了取搜解决办法
Sys.setenv(LANGUAGE = "en")
#安装CRAN下的包
install.packages("BiocManager")
#可能会报错构建R包需要Rtools但当前未安装。在继续之前请下载并安装相应版本的Rtools
#加载BiocManager包
library(BiocManager)
#安装Bioconductor下的包
BiocManager::install("GEOquery")
运行R包下的函数首先要加载R包
#加载GEOquery包
library(GEOquery)
##设置路径
getwd()#获取当前路径
setwd("E:\\Document\\RFiles") #用双斜杠
?getGEO #查看函数参数
##下载数据 getGPL = F 这个代表不下载平台注释文件因为有时候网络不稳定。后面我们会在网页中下载然后读取。
gset = getGEO('GSE12417', destdir=".",getGPL = F)
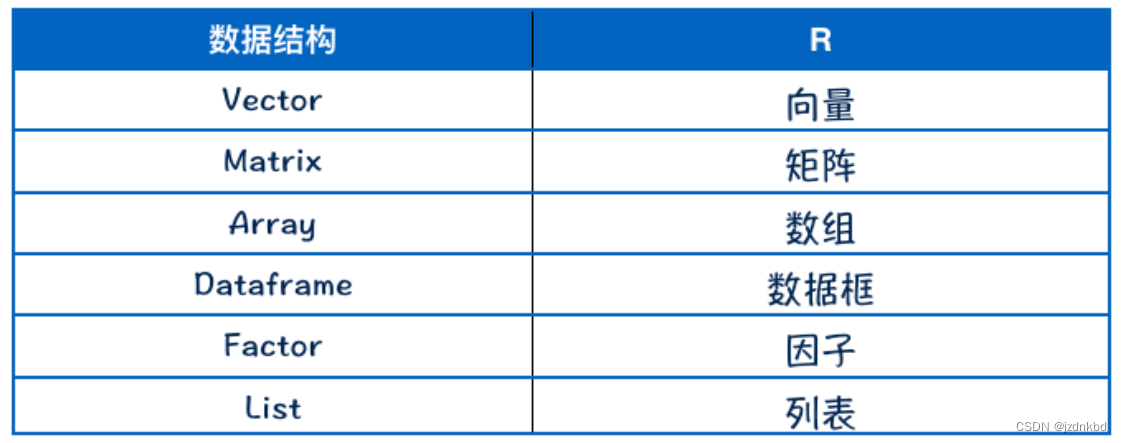
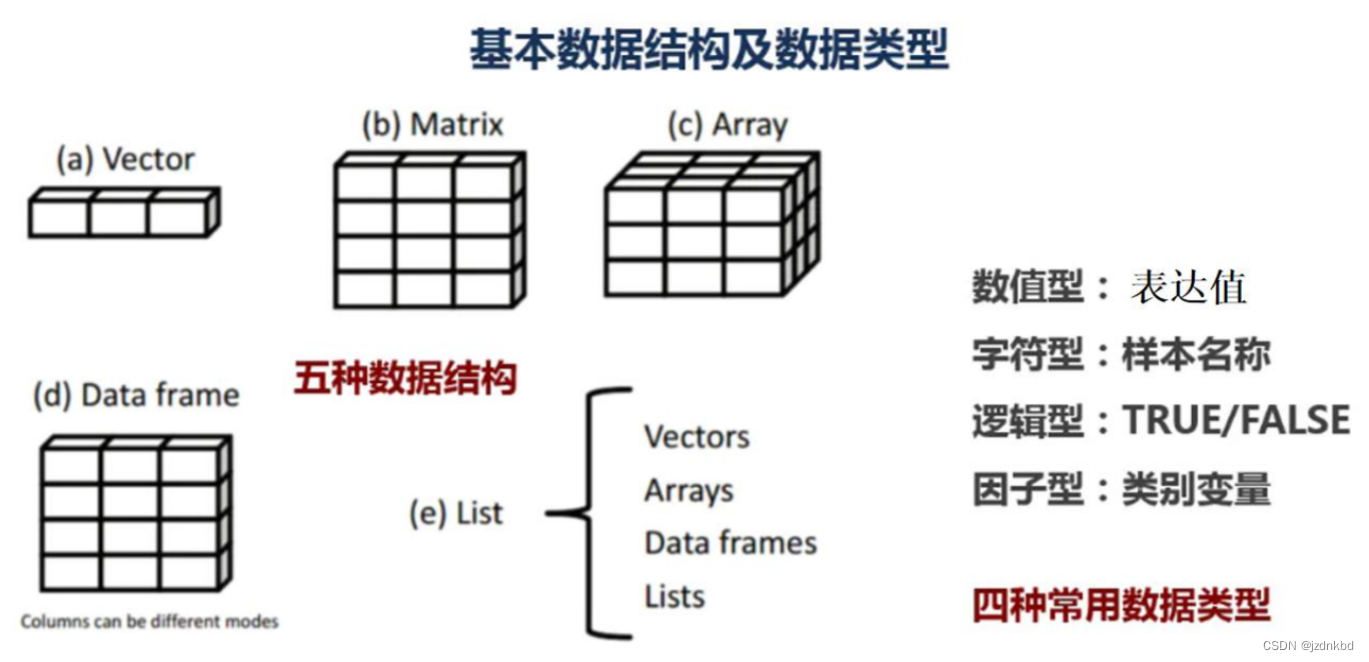
四.数据结构
1.向量Vector
向量是用于存储数值型、字符型或逻辑型数据的一维数组。
两个特点 1.有序性 2.存储单一数据类型
1.1创建向量
你需要认真学习以下函数
c(): 用来建立向量的函数
seq(): 该函数用于创建包含from~end数值的向量
rep(): 该函数用来创建保存重复值的向量
length(): 用来计算向量长度的函数
names(): 该函数用来对向量各元素命名。
我们可以用函数c()来创建向量。比如
a <- c(1,2,3,4,6,7,9,0)#存储数值型
b <- c("哎","哟","喂啊")#存储字符型
c <- c(TRUE, FALSE, TRUE, TRUE)#存储逻辑型
如果数据类型不同会自动转化为同一类型
可以用mode() 或 class()函数查看对象数据类
a <- c(7,TRUE);mode(a) #结果是"numeric"
b <- c(7,"哎");mode(b) #结果是"character"
c <- c(TRUE,"哎");mode(c) #结果是"character"
d <- c(7,TRUE,"哎");mode(d) #结果是"character"
无论什么类型的数据缺失数据总是用NA(不可用)来表示
如果想用键盘输入一些数据也是可以的只需要直接使用默认选项的scan()函数
z <- scan()
1.2访问向量中的数据
通过在[ ]中给出元素所在位置的数值我们就可以访问向量中的元素了。
有4种访问方式看下图

示例如下
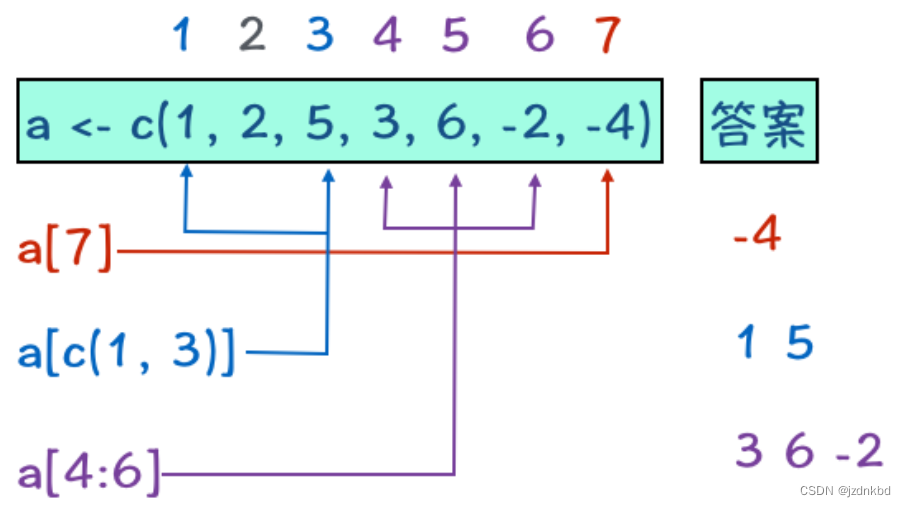
#删除第二个元素
a=a[-2]
x[-1]表示将第一个元素删除。但是既然说的是负整数如果非整数比如x[-0.5]也不会报错会默认删除第一个元素。x[-2.5]删除第二个元素。
空下标与零下标
x[ ]表示取x的全部元素作为子集。 这与x本身不同。
x[0]是一种少见的做法结果返回类型相同、长度为零的向量相当于空集。
1.3向量的循环补齐
两个向量长度相等时向量间的运算是相应位置的数字进行运算运算后结果返回原位置。
但如果长度不相等呢
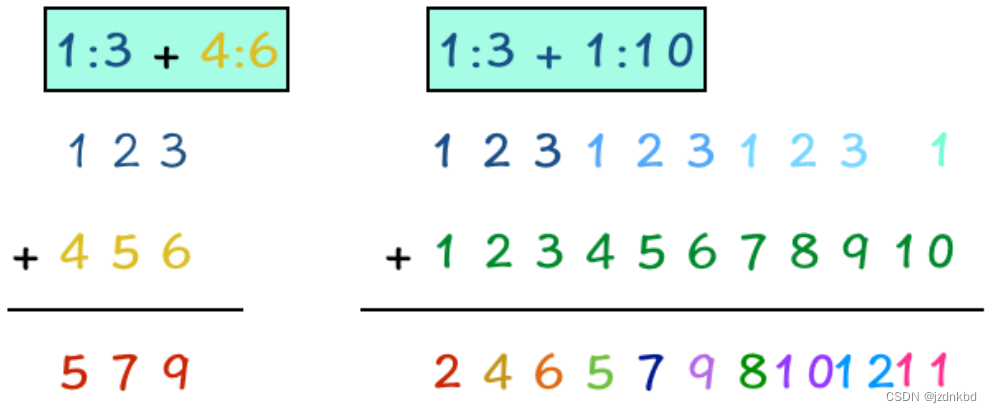
R会自动循环补齐也就是它会自动重复较短的向量直到与另外一个向量匹配
2.矩阵matrix
R中的矩阵与数学中的矩阵一样由指定的行row与列column构成。
和向量一样矩阵也只能保存同种数据类型的数据。
2.1创建矩阵
你需要认真学习以下函数
matrix(): 用来建立矩阵的函数
nrow():求矩阵的行数
ncol(): 求矩阵的列数
dim(): 求对象的维数
t(): 求矩阵的转置矩阵
solve(): 从方程a%*%x = b中求x。若不指定b 则求a的逆矩阵。

x=matrix(c(1,3,4,2,-9,4,7,0,8),ncol=3)
x

给出的数据个数要等于想要建立矩阵的元素个数才可以否则就会报错
函数rownames()和colnames()可以为矩阵指定行名和列名。比如
rownames(x)=c("Lisa","Bob","Jay")
colnames(x)=c("成绩1","成绩2","成绩3")
x
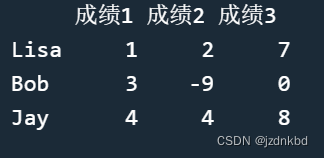
当没有行名时我们用rownames()查看行名会返回NULL
2.2访问矩阵中的数据
借助索引或行名与列名就可以访问矩阵中的数据

与向量类似哟如果索引是负数则表示排除指定行或列若索引为向量则可以从矩阵中一次获取多个值。若想获取整行或整列只要在指定行或列的位置上不写索引即可。
#获取第一行、第三行与第1列、第三列数据的交集
x[-2,-2]
#请使用行名、列名查出Bob的成绩2
x["Bob","成绩2"]

矩阵与标量、矩阵与矩阵间的四则运算如下表所示

除了简单的四则运算矩阵还有特殊的运算需要函数来帮忙。
我们用t()函数来求矩阵的转置矩阵
我们用solve(a, b)函数来为方程 a %*% x = b求解。其中 a为矩阵b为向量或矩阵
若不指定b则求 a的逆矩阵。
我们用nrow()函数来求矩阵的行数
我们用ncol()函数来求矩阵的列数
我们用dim()函数来求矩阵的维数当然也可以用它来设置矩阵维数。比如
#将3*2的矩阵x改为2*3并输出矩阵x
x <- matrix(c(1,3,4,2,-9,4), ncol=2)
x
dim(x) <- c(2,3)
x
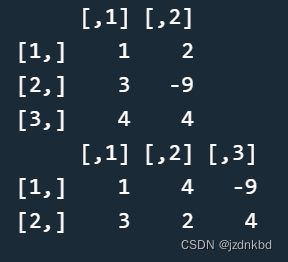
3数组Array
数组与矩阵类似但是维度可以大于2。
比如使用矩阵可以表现 2×3 维的数据而使用数组则可以表现 2×3×4 维的数据。
和向量、矩阵一样数组也只能保存同种数据类型的数据。
3.1创建数组
你需要认真学习以下函数
array(): 用来建立数组的函数
dim(): 求对象的维数。

array(1:12,dim=c(3,4))

对于4×3×2维的数组你们也可以理解为它创造了2个 4×3的矩阵。
x<-array(1:24,dim=c(4,3,2))

3.2访问数组中的数据
访问数组中数据的方法和矩阵类似因为他们只是维数不同而已。
所以要想访问数组元素我们一样可以使用索引、名称等进行访问。
x[1, , ]
x[ ,1, ]
x[ , ,1]
x[1,1, ]
x[ ,1,1]
x[1, ,1]
x[1,1,1]
4.数据框Dataframe
4.1创建数据框
你需要认真学习以下函数
data.frame(): 用来建立数据框的函数
str(): 查看数据框结构。
由于不同的列可以包含不同模式数值型、字符型的数据数据框的概念跟矩阵相比更为一般。
数据框是R中最常处理的数据结构。
数据框可以通过函数 data.frame(col1, col2, col3, …) 来创建。
其中列向量col1,col2,col3可为任何类型。
每一列数据的模式必须唯一不过你却可以将多个模式的不同列放到一起组成数据框。
比如执行以下代码后
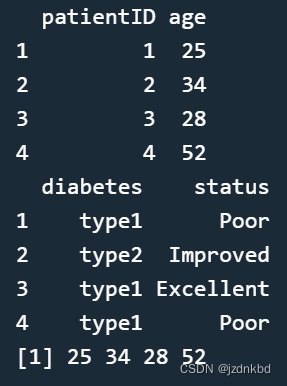
patientID <- c(1, 2, 3, 4)
age <- c(25, 34, 28, 52)
diabetes <- c("type1", "type2", "type1", "type1")
status <- c("Poor", "Improved", "Excellent", "Poor")
patientdata <- data.frame(patientID, age, diabetes, status)
patientdata
我们能得到结果

4.2访问数据框中的数据
我们可以像之前一样使用索引来访问数据框中的元素也可以用数据框特有的新办法来访问那就是 $ 符号。
patientdata[1:2]
patientdata[c("diabetes", "status")]
patientdata$age
下面是运行结果
函数str()可以查看数据框结构
str(patientdata)
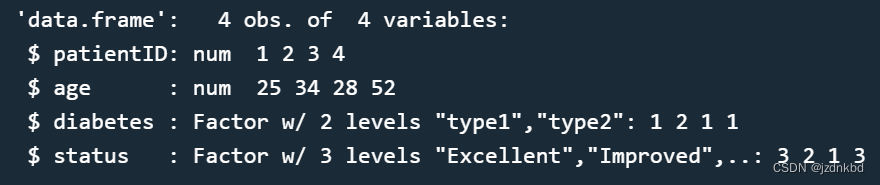 可以看到diabets和status是因子类型下面会讲。
可以看到diabets和status是因子类型下面会讲。
names()函数用于返回数据框点的列名。使用 %in%运算符与names()函数能够快速选取特定列。
patientdata[ ,names(patientdata)%in%c("patientID","diabetes")]

反之~使用 ! 运算符可以排除特定列
patientdata[ ,!names(patientdata)%in%c("patientID","diabetes")]
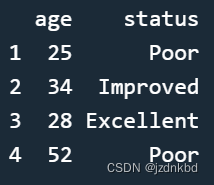
如果只访问一列会返回向量想避免这种类型转换的话只需要设置drop=FALSE即可
patientdata[ ,2]
patientdata[ ,2,drop=F]

5因子Factor
因子简单来说在 R 中因子就是分类数据。
比如说狗狗可以分类成“大型犬”“中型犬”“小型犬”那“狗狗”就是顺序型的因子它有3种水平level分别是“大型犬”“中型犬”“小型犬”。
那还有一些因子其实是无法比较大小的我们叫它名义型的因子比如政治倾向中的2种level“左派”和“右派”。
5.1创建因子
你需要认真学习以下函数
factor(): 用来建立因子的函数
nlevels(): 返回因子中的水平个数
levels(): 返回因子水平目录
ordered(): 创建有序因子。

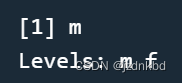
性别属于名义型数据有“m”male男性与“f”female女性两种可能的值。下面的例子中创建了性别的因子保存了男性的变量在sex中。
sex <- factor("m", c("m","f"))
sex
5.2访问因子中的数据
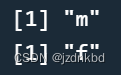
函数levels()可以获得因子水平的名称。
levels()返回的是向量所以我们可以用索引获得各水平值。
levels(sex)[1]
levels(sex)[2]
我们还可以修改因子变量中的水平值
还是用levels()函数
比如把“m”修改为“male”,“f"修改为"female”
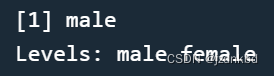
levels(sex)<-c("male","female")
sex
我们用nlevels()函数来获取因子水平个数
我们用ordered()函数来设置水平值的顺序。
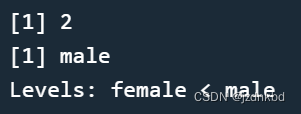
nlevels(sex)
ordered(sex,c("female","male")
6.列表List
列表list是R的数据类型中最复杂的一种。它什么都存
某个列表中可能是若干向量、矩阵、数据框甚至其他列表的组合。
6.1创建列表
R中的列表与其他语言中的散列表Hash table或字典Dictionary非常类似就是说列表是以“键值”对的形式保存数据的关联数组Associative Array。

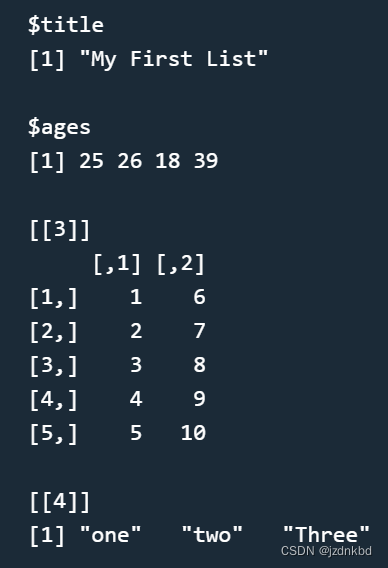
比如创建一个列表该列表有4个对象分别是g、h、j、k
其中对象 g 的 name 为 title对象 h 的 name 为 ages其他对象没有 name
g 为 标量字符串“My First List”
h 为数值向量包含元素 25261839
j 为 5*2 的矩阵元素为110
k 为字符串向量包含元素 “one”“two”“Three”
x=list(title="My First List",ages=c(25,26,18,39),matrix(1:10,nrow=5),c("one","two","Three"))
x
6.2访问列表中的数据
访问列表中的数据我们既可以使用索引又可以使用对象名。

输出列表时其中的每个对象都会以 $name 的形式罗列出来。使用 x $name形式可以访问对象的数据。
x[n]返回的是(name, value)的子列表不是value
而x[[n]]返回的是对象的value
#输出该列表的第二个对象的 value
x[[2]]
#输出该列表第三个对象
x[2]
#输出“ages”的value
x$ages

可以看到x[[[2]]]与x$ages结果一样
五.获取表达矩阵
library(GEOquery)
##下载数据 getGPL = F 这个代表不下载平台注释文件因为有时候网络不稳定。后面我们会在网页中下载然后读取。
gset = getGEO('GSE12417', destdir=".",getGPL = F)
View(gset)
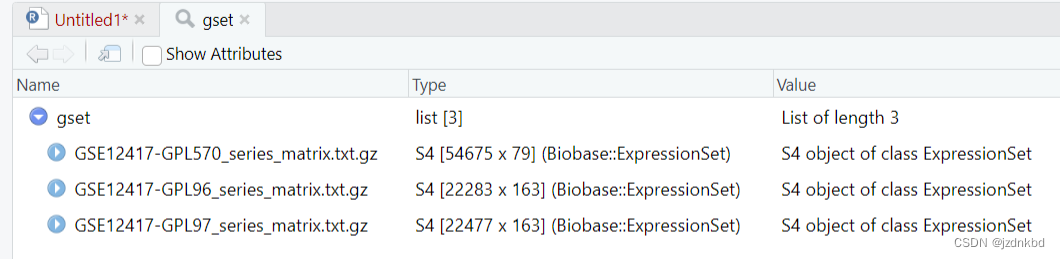
class(gset)
class(gset)
[[1]] “list”
可以看到gest对象是list类型数据提取list类型数据用 [[ ]]
#按序号提取GPL96
e2<-gest[[2]]
#按名字提取
e2<-gset[["GSE12417-GPL96_series_matrix.txt.gz"]]
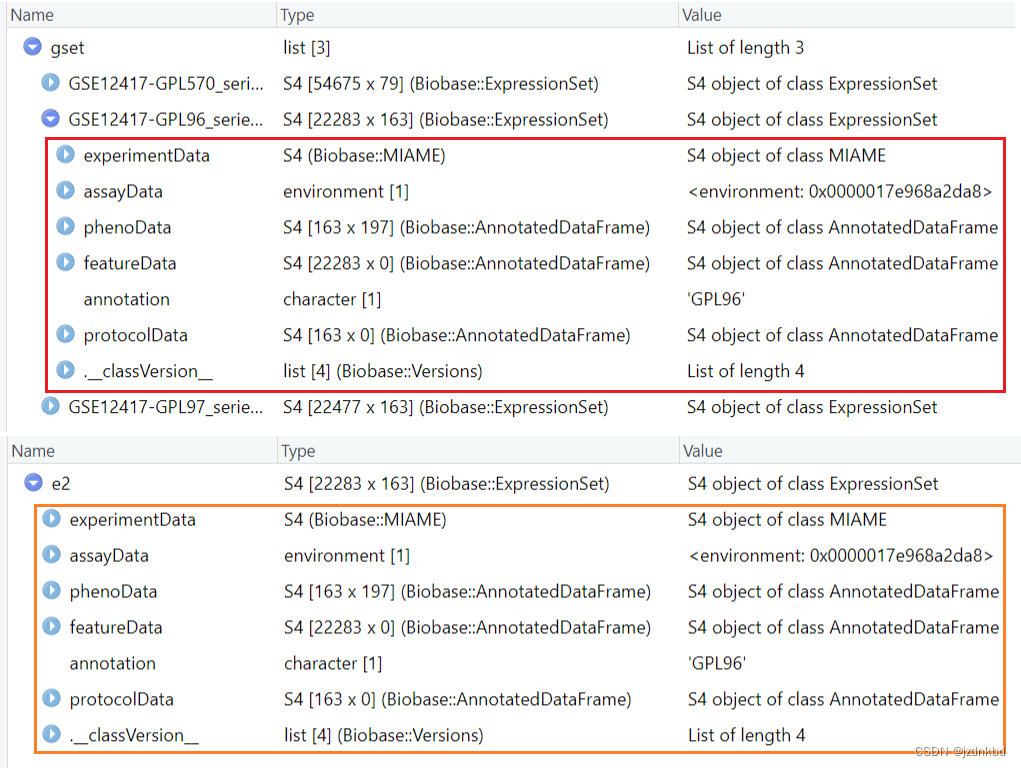
# s3:matrix 矩阵 data.frame() 数据框 character() 向量字符型 list 列表
# s4更复杂
s4对象提取
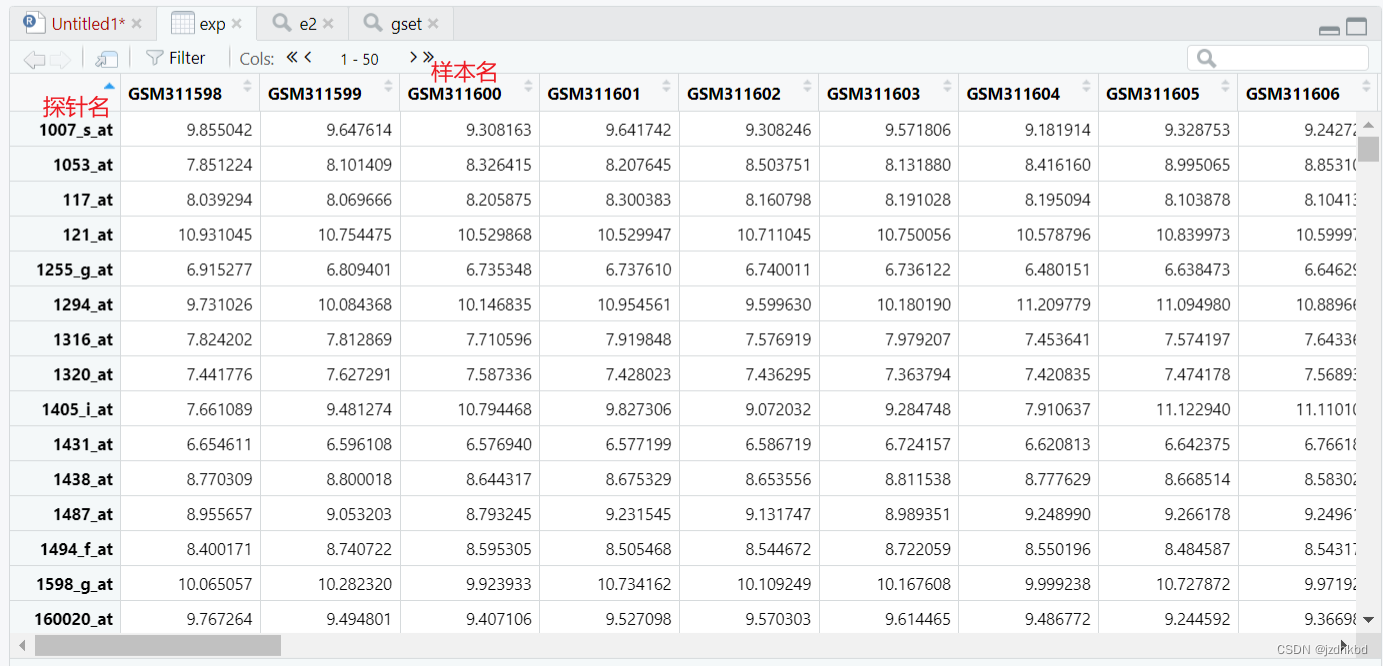
###提取表达矩阵
exp=exprs(e2)
##当然也可以用环境中的白色括号提取
exp2=e2@assayData[["exprs"]]
class(exp) #[1] "matrix" "array"
View(exp)
###用 @ 或 $符号
phe=e2@phenoData@data
phel=e2@phenoData@varMetadata$labelDescription
环境对象保存
save(gest,file="gset.rdata") #把gset对象保存为rdata数据文件
load("gset.rdata") #将这个对象文件加载到环境中
####或者用下面一对函数保存为rds文件
saveRDS(gset,file="gse12417.rds")
readRDS("gse12417.rds")
整理探针转化文件
#e2<-gset[["GSE12417-GPL96_series_matrix.txt.gz"]]
#e2是GPL96平台首先下载文件
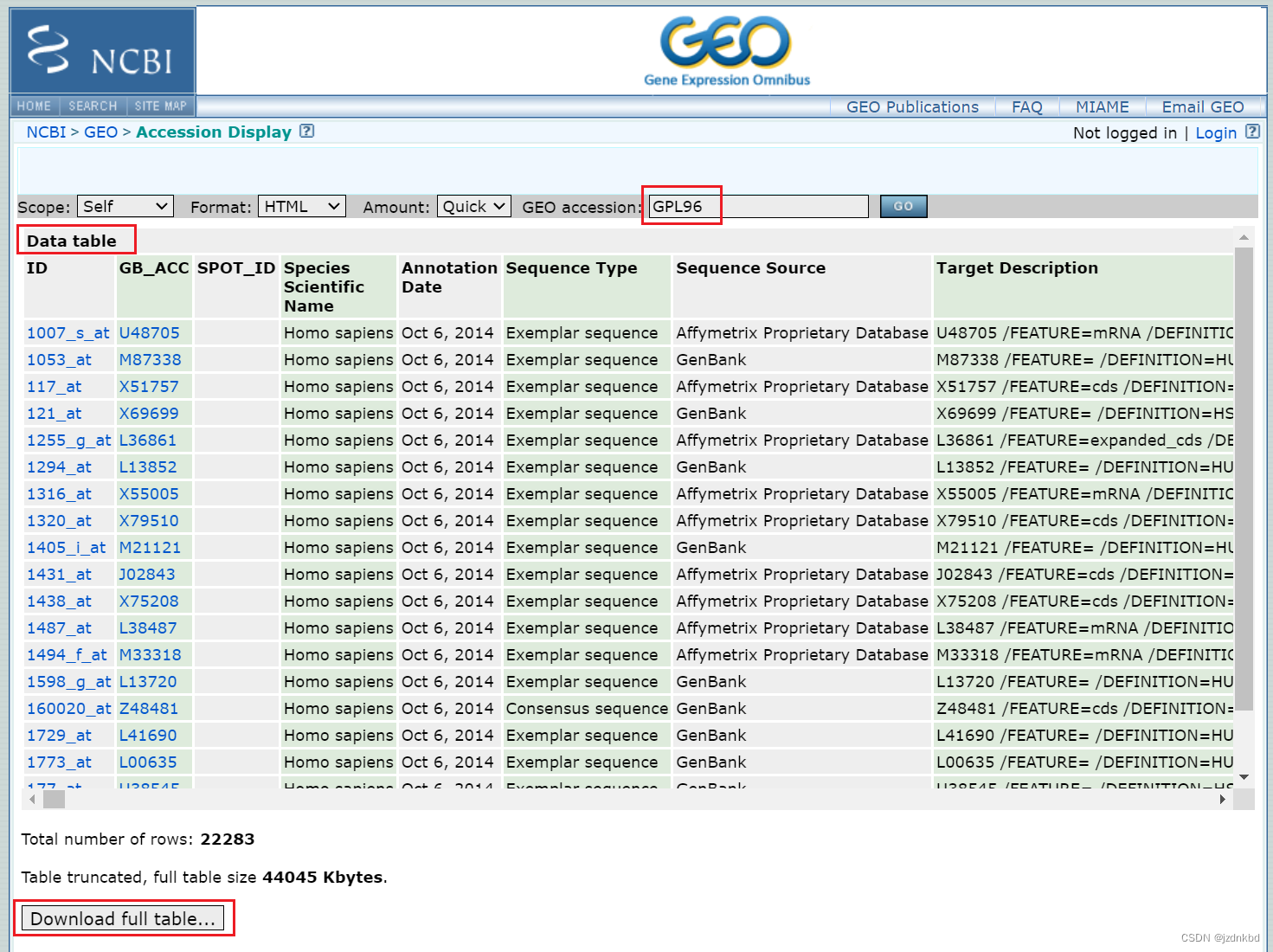
往右拉可以看到探针对应的基因名
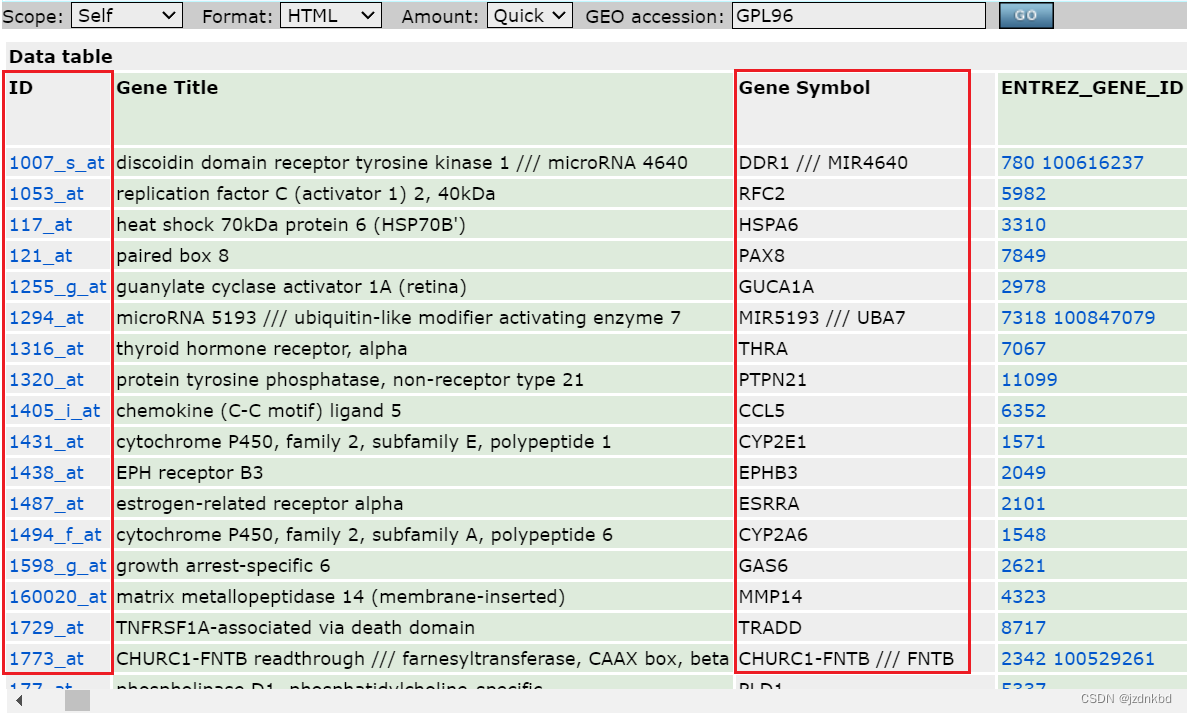
library(data.table)
#用里面 fread 函数读取txt文件
anno=fread("GPL96-57554.txt",header = T,data.table = F)
#用read,table读取
anno3=read.table("GPL96-57554.txt",sep="\t",header=T,fill=T)
class(anno)#[1] "data.frame"
View(anno)
x1=colnames(anno)
x2=rownames(anno)
未完待续。。。。
| 阿里云国内75折 回扣 微信号:monov8 |
| 阿里云国际,腾讯云国际,低至75折。AWS 93折 免费开户实名账号 代冲值 优惠多多 微信号:monov8 飞机:@monov6 |

