| 阿里云国内75折 回扣 微信号:monov8 |
| 阿里云国际,腾讯云国际,低至75折。AWS 93折 免费开户实名账号 代冲值 优惠多多 微信号:monov8 飞机:@monov6 |
最近TCGA更新了下载研究一下我们从TCGA下载STAD的数据选择其中的一个打开发现了一个好消息那就是矩阵的整合难度降低了而且提供TPM以及FPKM 还有校正的count 以及gene_name
在我的主页更新了TCGAbiolinks的方法更为方便和快捷。同时我也提供了临床数据的处理方式
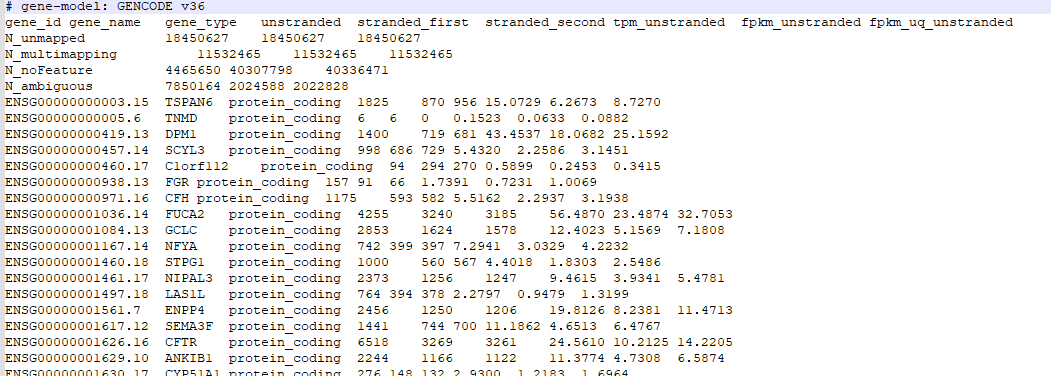
其实整理起来比较简单这里我没有使用python去写脚本使用R硬刚说实话头有点铁。
首先整理好你要的数据下载步骤跟以前一样当然不懂就去B站看新版TCGA介绍
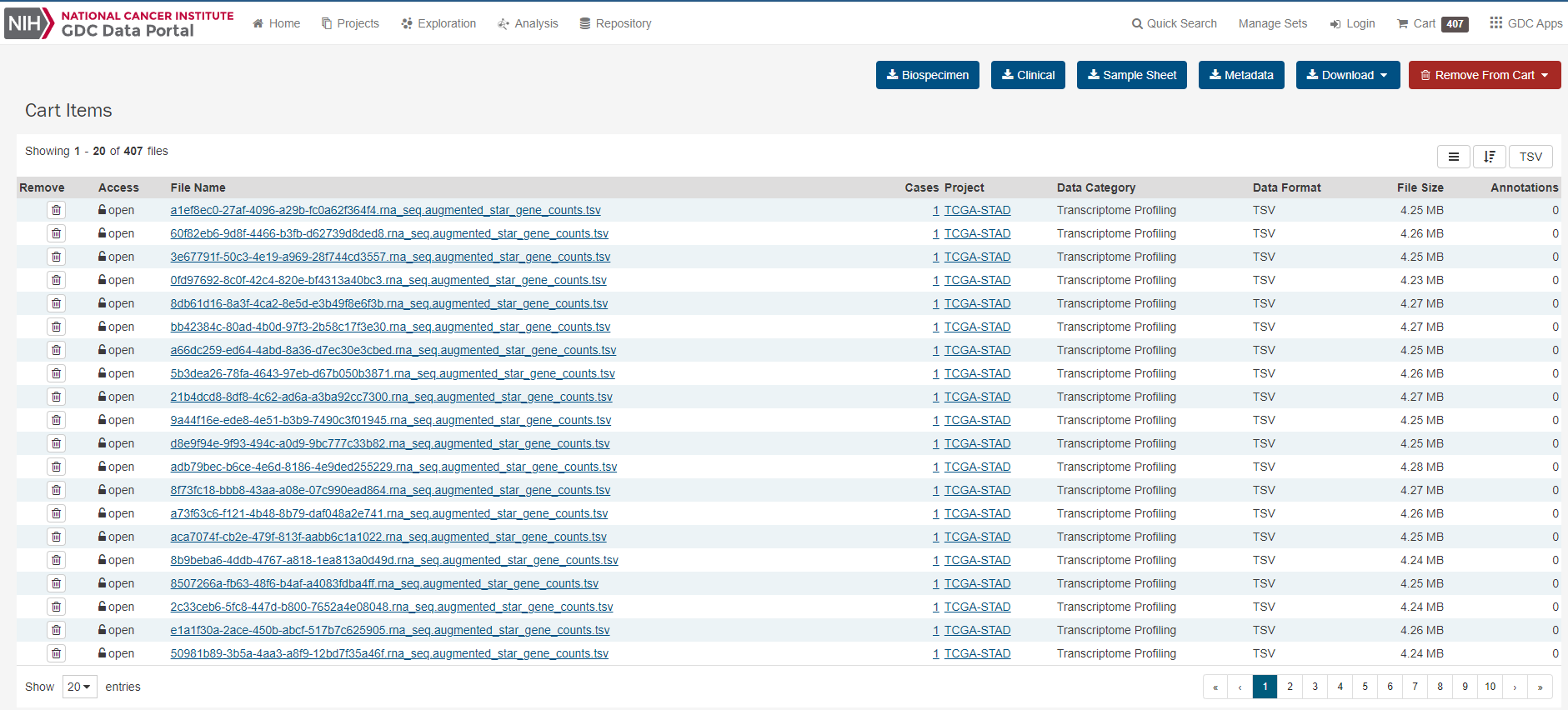
首先下载metadata
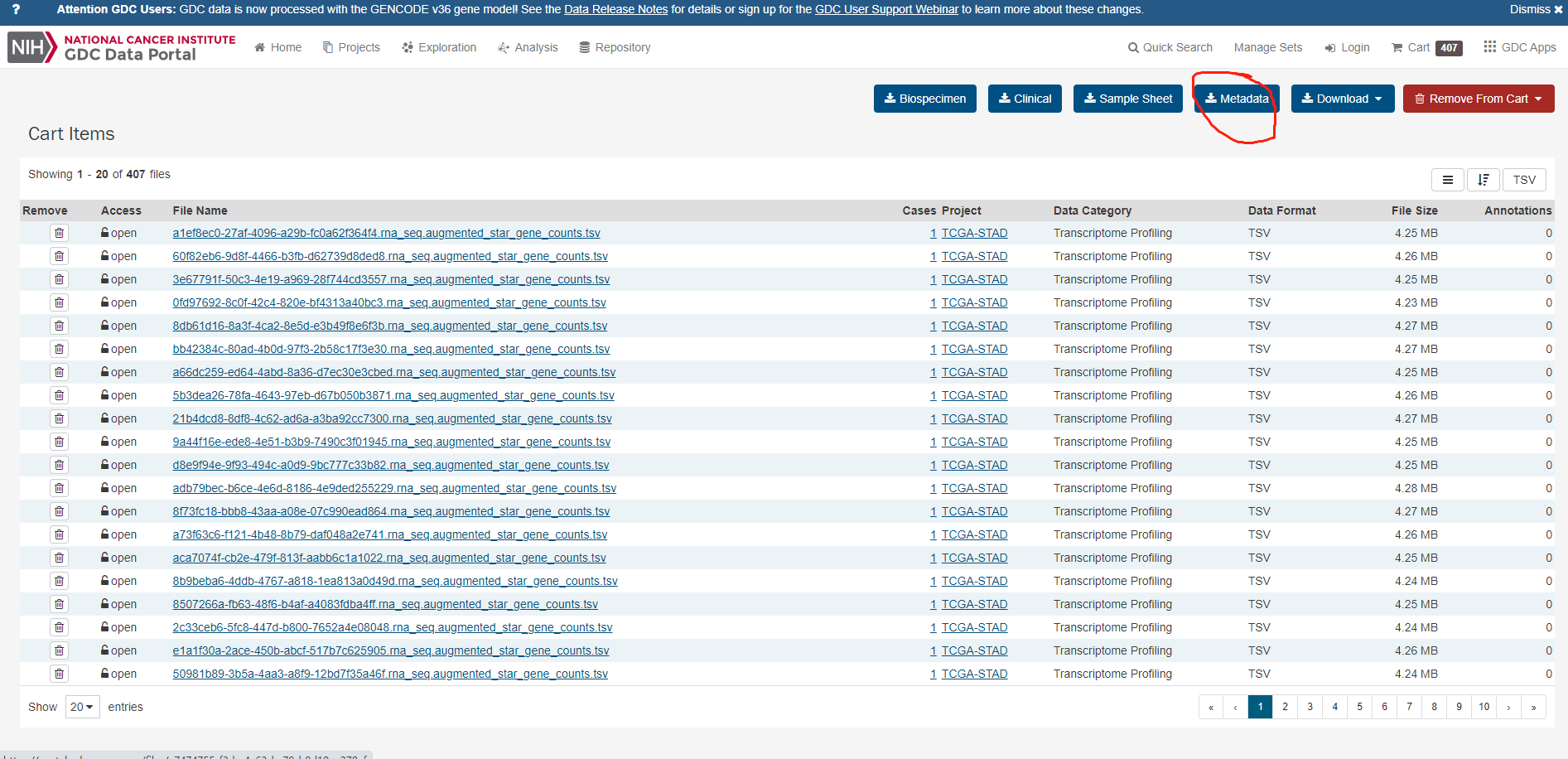
接着从download 中下载cart
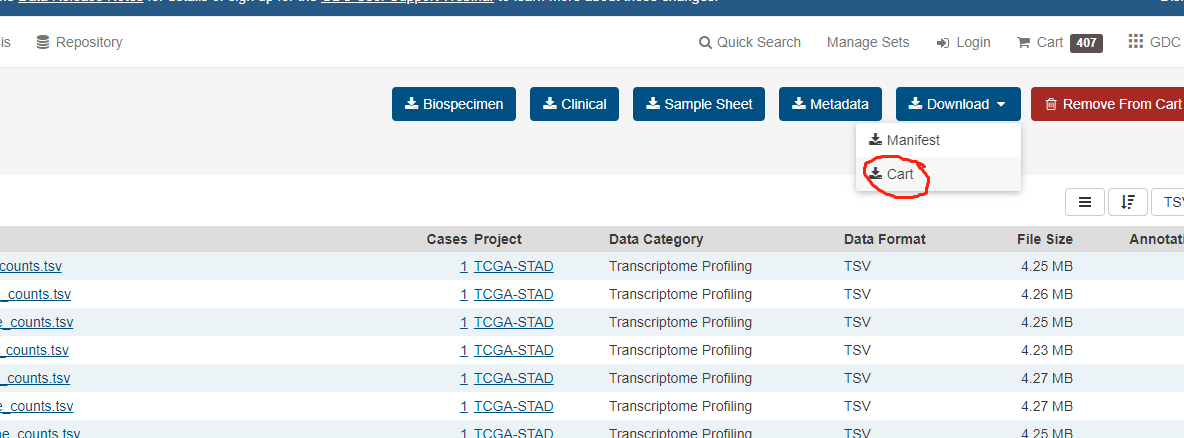
下载结束 之后解压随便打开一个文件我们的目的是整合tsv文件到一个文件夹

技巧教授如何整合呢windows下最简单的方式右上角搜索.tsv结尾的文件
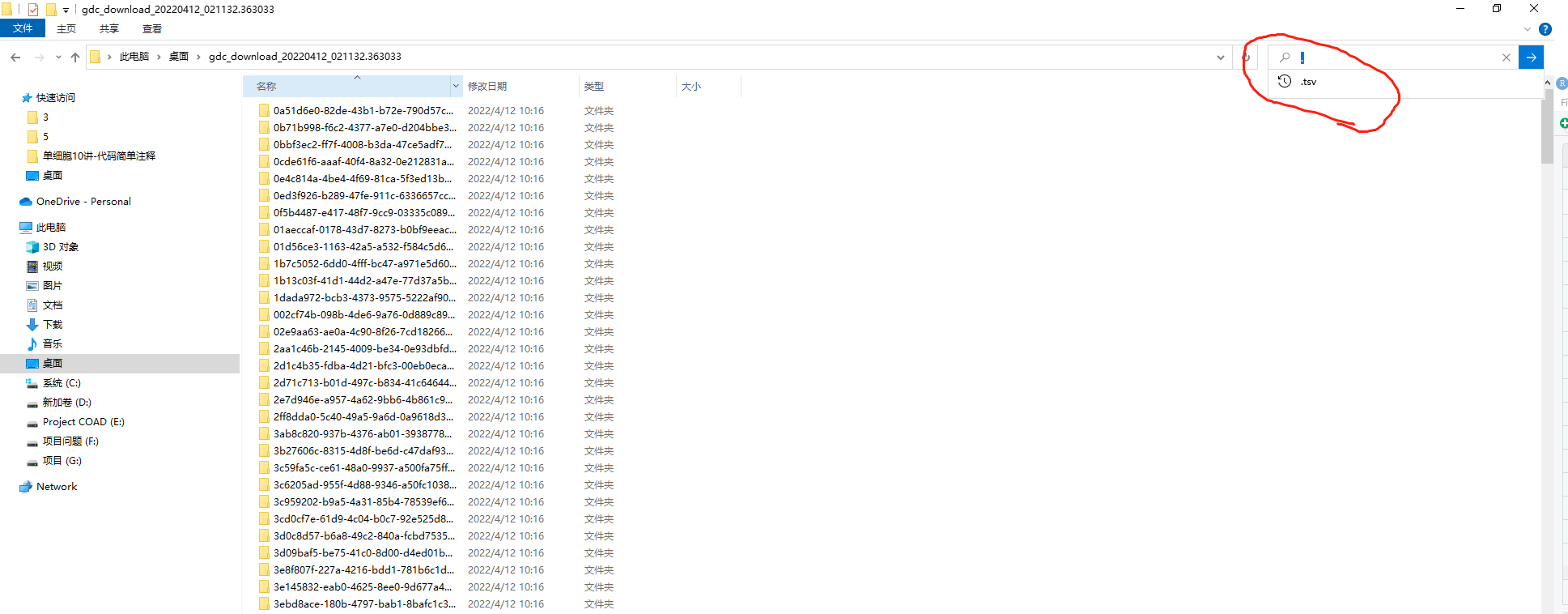
最后你就可以得到这个列表然后复制到一个文件夹里面最后有个MANIFEST.txt不要复制进去
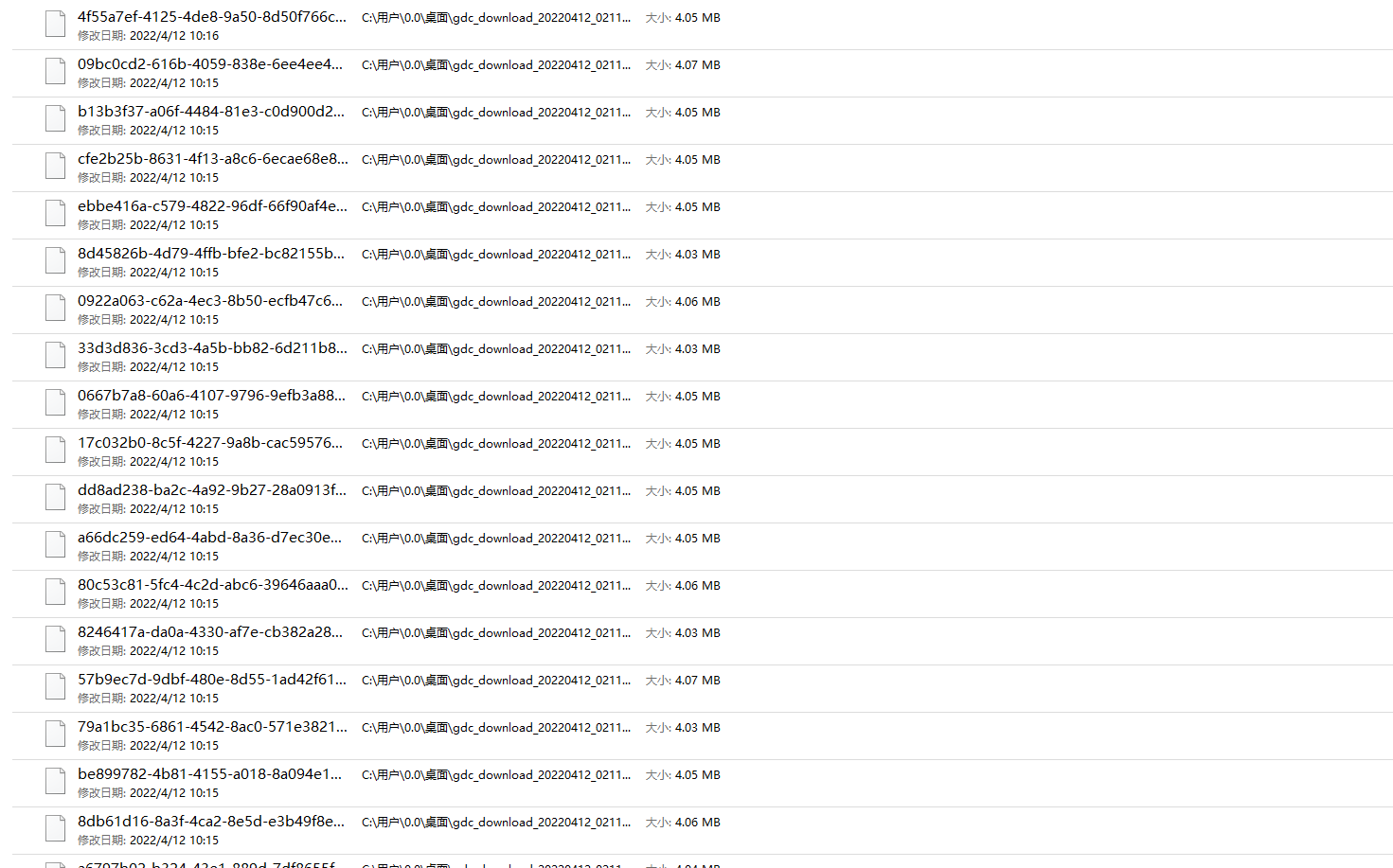
最后整理成下面的样式all文件夹是所有的tsv文件metadta上面介绍已经下载好了放进去

整理metadata文件
rm(list = ls())
options(stringsAsFactors = F)
library("rjson")
result <- fromJSON(file = "./metadata.cart.2022-04-12.json")
metadata <- data.frame(t(sapply(result,function(x){
id <- x$associated_entities[[1]]$entity_submitter_id
file_name <- x$file_name
all <- cbind(id,file_name)
})))
metadata[,2]
rownames(metadata) <- metadata[,2]
得到样本文件对应的TCGA的ID号
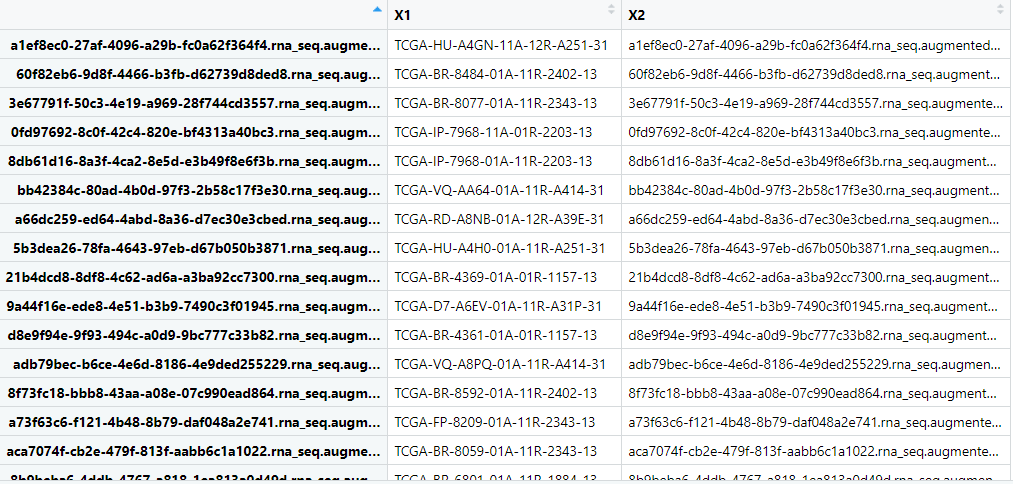
生成矩阵
dir <- './all/'
samples=list.files(dir)
sampledir <- paste0(dir,samples)
mat <- do.call(cbind,lapply(sampledir, function(x){
rt <- data.table::fread(x,data.table = F)
rownames(rt) <- rt[,1]
rt <- rt[,7]###后续方便不用再转换直接拿TPM
}))
这里需要读取一个单个tsv文件进行查看
可以看到我们上面代码中选择rt[ ,7] 是选择的tpm 需要的话可以你可以选择count和FPKM
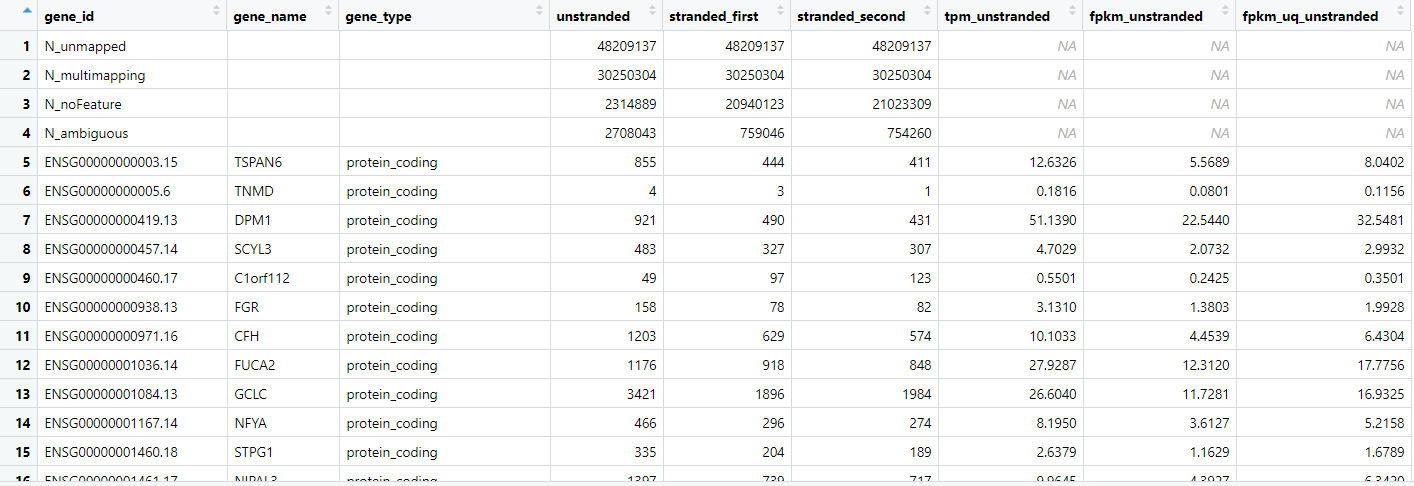
矩阵列明和行名的替换
###随便打开一个tsv文件即可
rt <- data.table::fread('./all/5c84144f-68b0-4f96-8b53-5a43a6f83847.rna_seq.augmented_star_gene_counts.tsv',data.table = F)###随便打开一个tsv文件即可
colnames(mat)=sapply(strsplit(sampledir,'/'),'[',3)###列名
rownames(mat) <- rt$gene_id ##行名
mat1 <- t(mat)
same <- intersect(row.names(metadata),row.names(mat1))
data <- cbind(metadata[same,],mat1[same,])
rownames(data) <- data[,1]
tcga_stad <- t(data)
tcga_stad <-tcga_stad[-c(1:6),]
rownames(rt) <- rt[,1]
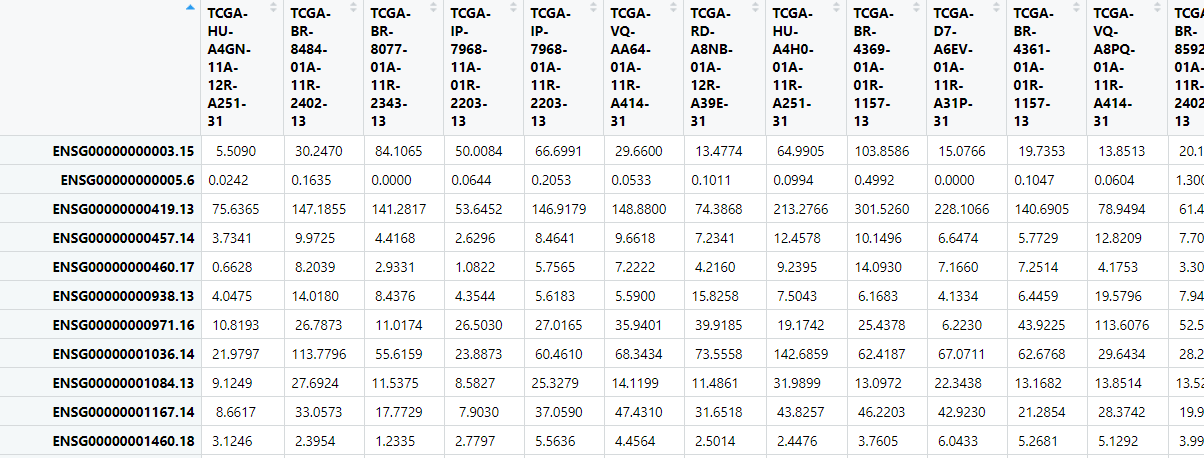
最后那必须是如何ID的转换 根据自带的信息我们进行转换这次的更新就是ID给了对照基因名真好还有类型妈的TCGA良心一次更新
same2 <- intersect(row.names(rt),row.names(tcga_stad))
tcga <- cbind(rt[same2,],tcga_stad[same2,])
tcga <- tcga[-c(1,4:9)]
到此你们自己保存文件把然后正常的基因去重问题这个应该搜索一下 也可以再我的博客里面看看
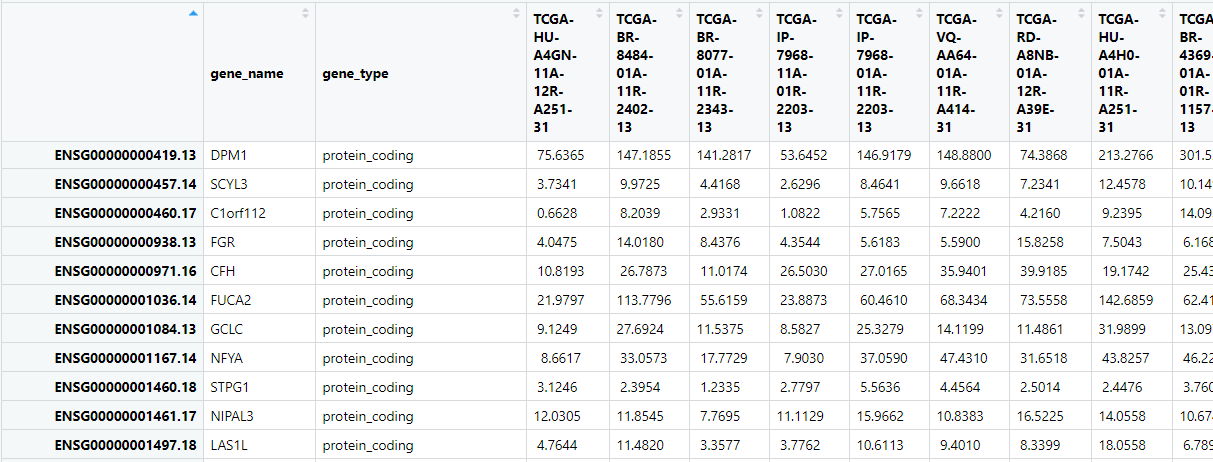
##要把上面的gene_type删除
rt = tcga[,-2]
rt=as.matrix(rt)
rownames(rt)=rt[,1]
exp=rt[,2:ncol(rt)]
dimnames=list(rownames(exp),colnames(exp))
data=matrix(as.numeric(as.matrix(exp)),nrow=nrow(exp),dimnames=dimnames)
data=avereps(data)
data=data[rowMeans(data)>0,]
到此你们应该得到都会处理的矩阵了把














